
Databáze genových sad/pathways
Pro analýzu genových sad je potřebné nejdříve získat informace, které geny patří do kterých genových sad - tyto jsou obvykle v různých databázích:
1. Gene Ontology (GO) databáze. Je to hierarchická databáze, kde rodičovské uzly jsou obecnější termíny, naopak dceřiné uzly jsou více specifické. Na konci této hierarchie jsou geny/proteiny. Na samém vrcholu databáze jsou 3 rodičovské uzly:
Biologické procesy
Molekulární funkce
Buněčné složky
2. KEGG: = Kyoto Encyclopedia of Genes and Genomes. Svého času jedna z nejlépe udržovaných databází, teď už několik let neaktualizovaná (pouze v placené verzi) Obsahuje více informací než GO, jsou zde již zachyceny vztahy mezi geny a genovými produkty. Detailní informace jsetu však pouze pro některé organismy a procesy. Využívá hlavně ověřené poznatky a nemůže ji měnit kdoliv. Proto zde nejsou všechny geny (obvykle jen třetina až polovina z hledaných). Databáze navíc již není aktualizovaná.
příklad výstupu:
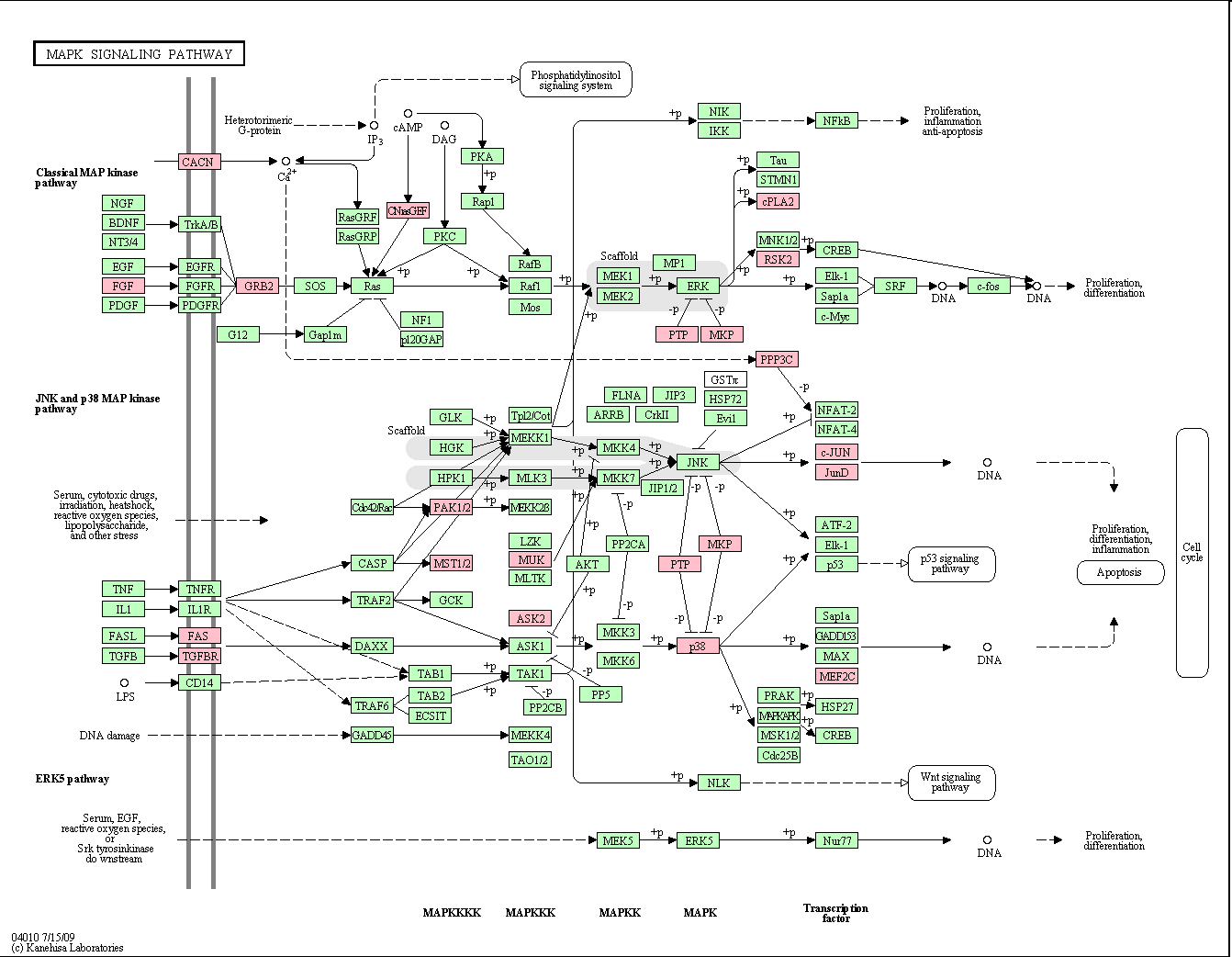
Poklikáním na jednotlivé uzly se zobrazí více informace o jednotlivých genech, jako například všechny ostatní dráhy, do kterých gen patří, identifikace daného genu v dalších databázích, odkaz na literaturu, ze které byly informace čerpány, případně další důležité články a samozřejmě informaci o sekvenci. Také je možné zabarvit jednotlivé geny podle různých barev.
3. MsigDB - databáze Broad Institute - obsahuje různé typy gneových sad. Co je nejzajímavější je, že také genové sady z publikací - genové signatury, odlišně exprimované geny mezi skupinami a podobně. Také obsahuje přímo nástroj pro analýzu genových sad přímo online. Tato databáze také poskytuje R kód a R balík pro analýzu genových sad.
4. DAVID - NIH databáze - podobně jako MsigDB, ale obsahuje genové sady nejen pro člověka, ale pro velké množství druhů. Také poskytuje analýzu genových sad online nebo propojení s R.




